DNA序列编码中Hairpin的定义和计算
DNA序列编码中Hairpin的定义和计算
觉得有用的话,欢迎一起讨论相互学习~Follow Me
参考文献
[1] 张凯. DNA计算核酸编码优化及算法设计[D]. 2008.
[2] Shin, Soo Yong , et al. "Multiobjective evolutionary optimization of DNA sequences for reliable DNA computing." IEEE Transactions on Evolutionary Computation 9.2(2005):143-158.
[3] Shin, Soo Yong , I. H. Lee , and B. T. Zhang . "Evolutionary Multi-Objective Optimization for DNA Sequence Design." (2008).
[4] Shin, Soo Yong , et al. "Evolutionary sequence generation for reliable DNA computing." Congress on Evolutionary Computation IEEE, 2002.
[5] 饶泽书. 基于多目标粒子群的DNA编码算法研究[D]. 2018.
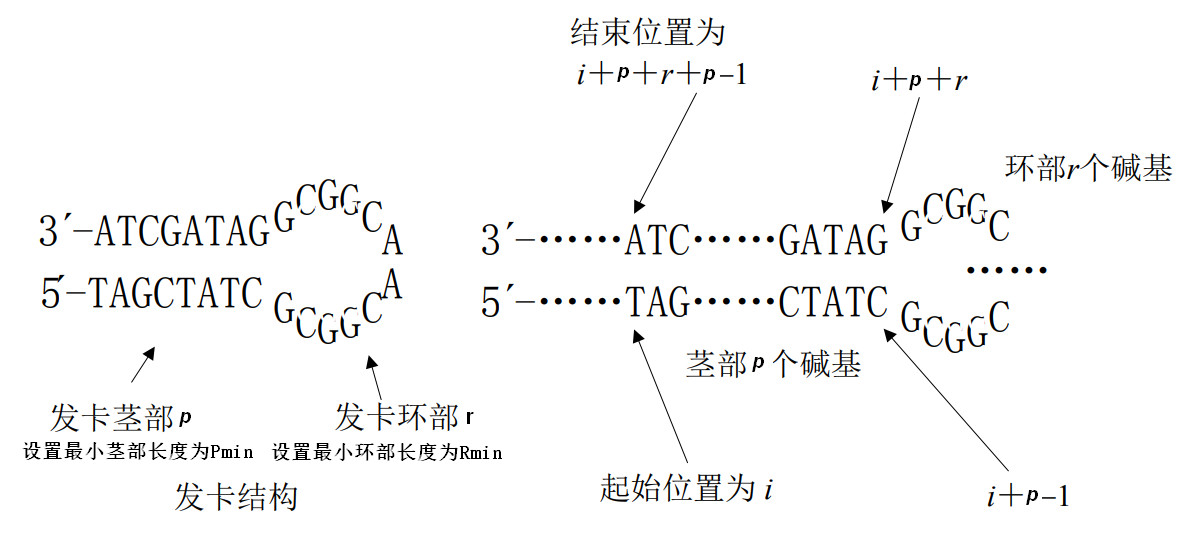
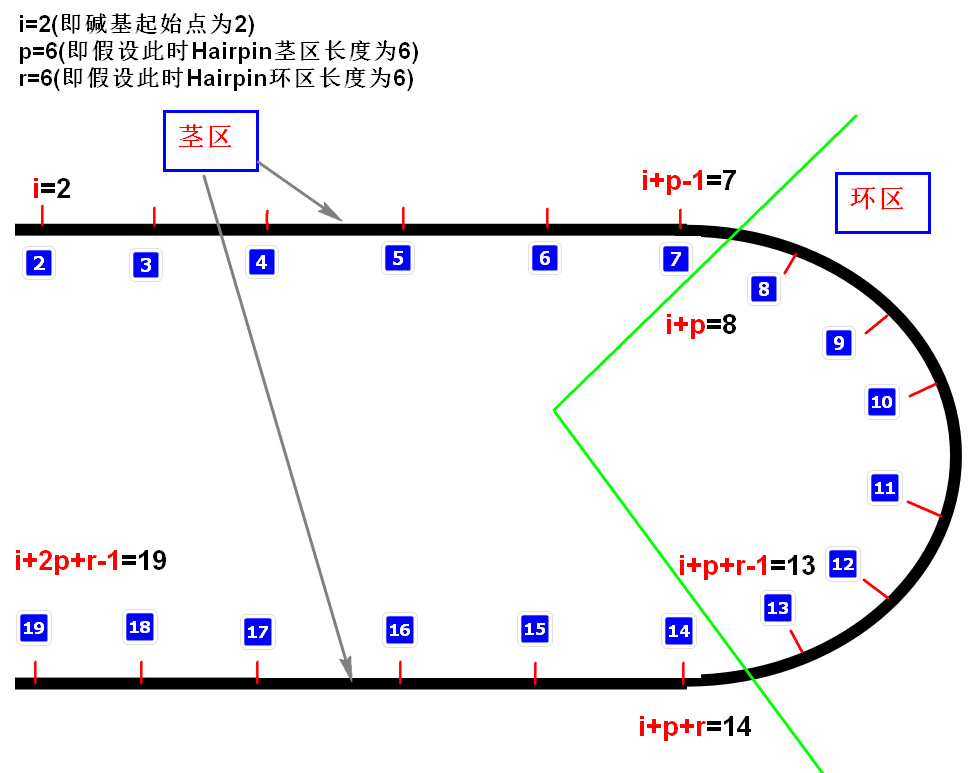
发卡结构约束
[ * ]定义
单链 DNA 分子产生二级结构通常由自身反向折叠而形成,发卡结构为典型的自身折叠结构.许多以特异性杂交反应为基础的 DNA 计算模型,都要求避免单链 DNA 形成二级
结构,这样单链 DNA 分子才能和自身的补链充分有效的发生特异性杂交[1]。
\[Hairpin( x ) = \sum _ { s = S _ { \mathrm { min } } } ^ { \left( l - R _ { \mathrm { min } } \right) / 2 } \sum _ { r = R _ { \mathrm { min } } } ^ { l - 2 s } \sum _ { i = 1 } ^ { l - 2 s - r } T \left( \sum _ { j = 1 } ^ { s } b p \left( x _ { s + i - j} , x _ { s + i + r + j-1} \right) , \frac { s } { 2 } \right)\]
- 式中s为茎长,Smin为设定的最小茎长。r为环长,Rmin为设定的最小环长,L表示DNA序列长度。在本文中,设置Smin=6,Rmin=6
- T表示阈值函数,T(x,y),只有在x>y时T(x,y)=x;否则T(x,y)=0,此处表示只有连续匹配达到了当前茎区数量的1/2(即>\(\frac{S}{2}\))才能算作为茎区的结构。
- bp(x,y)函数表示DNA序列中x和y位置的碱基相互互补的个数,如果相互互补即为1,否则记为0.
- s表示遍历茎区可能长度,其中 茎区最小长度为人为设定的Smin ,而 茎区最大长度是当环区长度取得最小值Rmin时的茎区长度(l-Rmin)/2
- r表示遍历环区可能长度,其中 环区最小长度为人为设定的Rmin ,而 **环区最大长度是当茎区长度取得最小值Smin时的环区长度l-2*Smin**
- i表示DNA序列起始处的索引,其中i最小从1处开始,最大可以到l-2s-r处,其中s和r皆为前两步中确定的值。
不同文章中发卡结构约束的定义及区别
上一章中定义此处标记为 [*]定义 而与其他定义相区别,其他定义则根据其引用的参考文献进行标记,即若此处定义出自于参考文献[1],则将其标记为 [1]定义
[2]定义

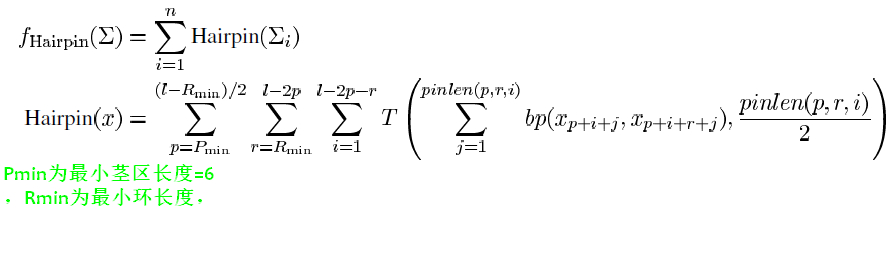
- 这个pinlen(p,r,i)很奇怪,定义为当假结中心在(p+i+r/2)时,可能的最大的茎区配对可能数 , 在作者2008发表的文章[3]中指出pinlen即为当前假定
的茎区数。 ==但是\(x_{p+i+j}和x_{p+i+r+j}的位置并不是假结茎区中一一对应的,[ * ]定义中是一一对应的关系\)==
[3]定义
- 在S.Y.Shin于2008年发表的[3]文章中,提出了如下定义:
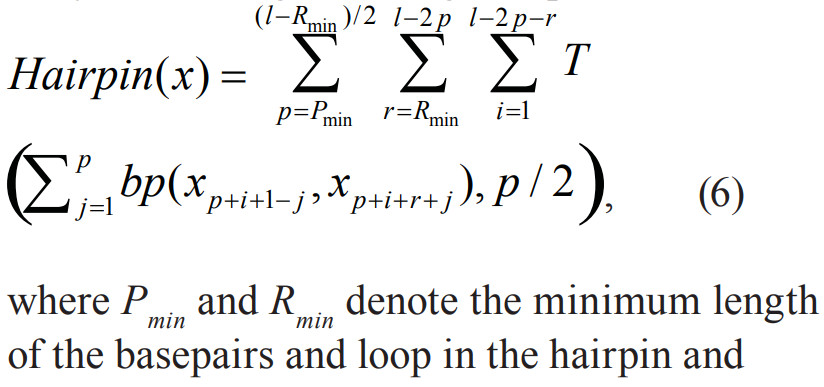
==[3] 定义与 [ * ]定义差别在于 [3] 定义中茎区匹配索引比 [ * ] 中均索引大1.==
[4]定义
- 在S.Y.Shin于2002年发表的[4]文章中,提出了如下定义:

其中Hairpin(x,c)函数没有明确的数学定义。仅仅是给出一个概念。
[5]定义
- \[\operatorname { Hairpin } ( x ) = \sum _ { s = S _ { \min } } ^ { \left( l - R _ { \mathrm { min } } \right) / 2 } \sum _ { r = R _ { \min } } ^ { l - 2 s } \sum _ { i = 1 } ^ { l - 2 s - r } T \left( \sum _ { j = 1 } ^ { s } b p \left( x _ { s + i - j } , x _ { s + i + r + j } \right) , \frac { S } { 2 } \right)\]
与[ * ]的区别在于\(x _ { s + i - j } , x _ { s + i + r + j }[5],x _ { s + i - j } , x _ { s + i + r + j-1 }[ * ]\)
分析与比较
可以看出[ * ]中Hairpin的计算公式较为正确
| No | J index | Expression x | Expression y |
|---|---|---|---|
| ==*== | - | \(x _ { s + i - j}\) | \(x _ { s + i + r + j-1}\) |
| - | j=1 | \(x_{s+i-1}\) | \(x_{s+i+r}\) |
| - | j=s | \(x _ {i}\) | \(x _ { i + r + 2s-1}\) |
| 2 | - | \(x_{s+i+j}\) | \(x_{s+i+r+j}\) |
| - | j=1 | \(x_{s+i+1}\) | \(x_{s+i+r+1}\) |
| - | j=s | \(x_{i+2s}\) | \(x_{i+r+2s}\) |
| 3 | - | \(x _ { s + i - j+1}\) | \(x _ { s + i + r + j}\) |
| - | j=1 | \(x_{s+i}\) | \(x_{s+i+r+1}\) |
| - | j=s | \(x _ {i+1}\) | \(x _ { i + r + 2s}\) |
| 5 | - | \(x _ { s + i - j}\) | \(x _ { s + i + r + j}\) |
| - | j=1 | \(x_{s+i-1}\) | \(x_{s+i+r=1}\) |
| - | j=s | \(x _ {i}\) | \(x _ { i + r + 2s}\) |
DNA序列编码中Hairpin的定义和计算的更多相关文章
- 在博客文章中使用mermaid 定义流程图,序列图,甘特图
概述 Mermaid(美人鱼)是一套markdown语法规范,用来在markdown文档中定义图形,包括流程图.序列图.甘特图等等. 它的官方网站是 https://mermaid-js.github ...
- [LeetCode] Repeated DNA Sequences 求重复的DNA序列
All DNA is composed of a series of nucleotides abbreviated as A, C, G, and T, for example: "ACG ...
- 华为OJ平台——DNA序列
题目描述: 一个DNA序列由A/C/G/T四个字母的排列组合组成.G和C的比例(定义为GC-Ratio)是序列中G和C两个字母的总的出现次数除以总的字母数目(也就是序列长度).在基因工程中,这个比例非 ...
- DNA序列对齐问题
问题描述: 该问题在算法导论中引申自求解两个DNA序列相似度的问题. 可以从很多角度定义两个DNA序列的相似度,其中有一种定义方法就是通过序列对齐的方式来定义其相似度. 给定两个DNA序列A和B,对齐 ...
- [DeeplearningAI笔记]序列模型1.1-1.2序列模型及其数学符号定义
5.1循环序列模型 觉得有用的话,欢迎一起讨论相互学习~Follow Me 1.1什么是序列模型 在进行语音识别时,给定了一个输入音频片段X,并要求输出片段对应的文字记录Y,这个例子中的输入和输出都输 ...
- python实现DNA序列字符串转换,互补链,反向链,反向互补链
在生物信息学分析中,经常对DNA序列进行一系列操作,包括子序列截取,互补序列获取,反向序列获取,反向互补序列获取.在python语言中,可编写如下函数完成这些简单功能. 子序列截取 python中对序 ...
- Leetcode 187.重复的DNA序列
重复的DNA序列 所有 DNA 由一系列缩写为 A,C,G 和 T 的核苷酸组成,例如:"ACGAATTCCG".在研究 DNA 时,识别 DNA 中的重复序列有时会对研究非常有帮 ...
- [LeetCode] 187. Repeated DNA Sequences 求重复的DNA序列
All DNA is composed of a series of nucleotides abbreviated as A, C, G, and T, for example: "ACG ...
- 利用Python【Orange】结合DNA序列进行人种预测
http://blog.csdn.net/jj12345jj198999/article/details/8951120 coursera上 web intelligence and big data ...
随机推荐
- MyBatis最初的程序解读---API
API详解: * 线程安全问题出现的条件 (1) 只有单例对象才可能出现线程安全问题 (2) 多线程环境,即多个线程会共享这个单例对象 ...
- UE4官方行为树快速入门文档解析和修改
近学习了UE4官方文档的行为树快速入门指南,发现里面的部分逻辑稍稍有点混乱和重叠,于是加入了自己的想法,修改了部分行为树逻辑,优化了其AI寻路能力. 初始的基本操作和资源创建同官方文档一样:1个Fol ...
- 初次接触OSSEC
OSSEC是一款开源的系统监控平台.它集成了HIDS(主机入侵检测).日志监控.安全事件管理(SIM).安全信息和事件管理(SIEM)于一身,结构简单.功能强大的开源解决方案. 主要优点 满足合规性 ...
- mysql学习(2)-Navicat Premium 12 链接MySQL8.0.11数据库报2059错误
Navicat Premium 12 链接MySQL8.0.11数据库报2059错误 1,问题现象 安装完MySQL8.0.11和Navicat Premium12后,我们会用Navicat去测试连接 ...
- Linux内核分析:完成一个简单的时间片轮转多道程序内核代码
PS.贺邦 原创作品转载请注明出处 <Linux内核分析>MOOC课程 http://mooc.study.163.com/course/USTC-1000029000 1.m ...
- mysql 插多行数据
应用场景: 需要把一个表(tableA)的个别字段筛选出来,添加到新表中(tableB).新表还含有其他字段,主键是uuid. 思路解析: 熟悉插入一行数据的sql语句: insert into cu ...
- 软件工程团队项目第一次Sprint评审
第一组:9-652 作品:炸弹人 评价:已经完成了界面的设计和基本功能,游戏已初具雏形.这款游戏可玩性很强,是个很不错的项目.但是对游戏并没有进行深入开发,不能持续的吸引玩家的兴趣,容易引起玩家的厌倦 ...
- Haskell(一 )------ Windos下环境配置
1.去官网下载安装包 2.然后运行安装包路径最好就不要改了. 3.打开命令行输入 cabal user-config init 会出现默认的放置配置文件的地址,然后到那个文件夹下修改config文件. ...
- [转载]ValidationExpression验证规则
ValidationExpression验证规则 在ASP.NET中,ValidationExpression 验证规则属性可以根据自已的需要,对输入的数据进行限制,其常用符号如下表所示: 符号 ...
- 团队伊始——DreamCatcher
我们的团队,队名是DreamCatcher,中文意思是追梦人,它是一首歌曲,所属专辑是<新世纪的曙光>. 这是一首很好听的歌曲,里面有一句歌词是: I'm a dream catcher ...
