寻找与疾病相关的SNP位点——R语言从SNPedia批量提取搜索数据
SNP是单核苷酸多态性,人的基因是相似的,有些位点上存在差异,这种某个位点的核苷酸差异就做单核苷酸多态性,它影响着生物的性状,影响着对某些疾病的易感性。SNPedia是一个SNP调査百科,它引用各种已经发布的文章,或者数据库信息对SNP位点进行描述,共享着人类基因组变异的信息。我们可以搜索某个SNP位点来寻找与之相关的信息,也可以根据相关疾病,症状来寻找相关的SNP。
初次使用SNPedia
SNPedia主页网址为http://snpedia.com/index.php/SNPedia,比如我想查找与crouzon综合症相关的SNP,只需要在SNPedia中搜索crouzon syndrome,即会出现许多相关的SNP搜索结果

如果这时候我想看每个SNP的相关信息,我就要每个链接分别点进去
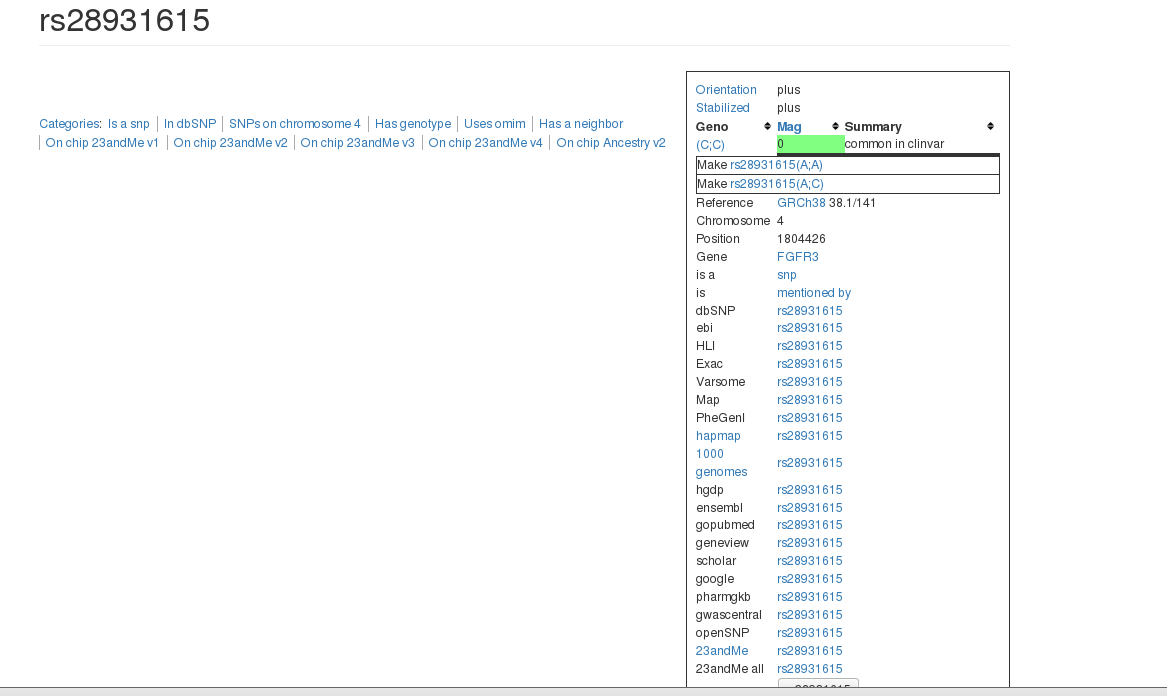
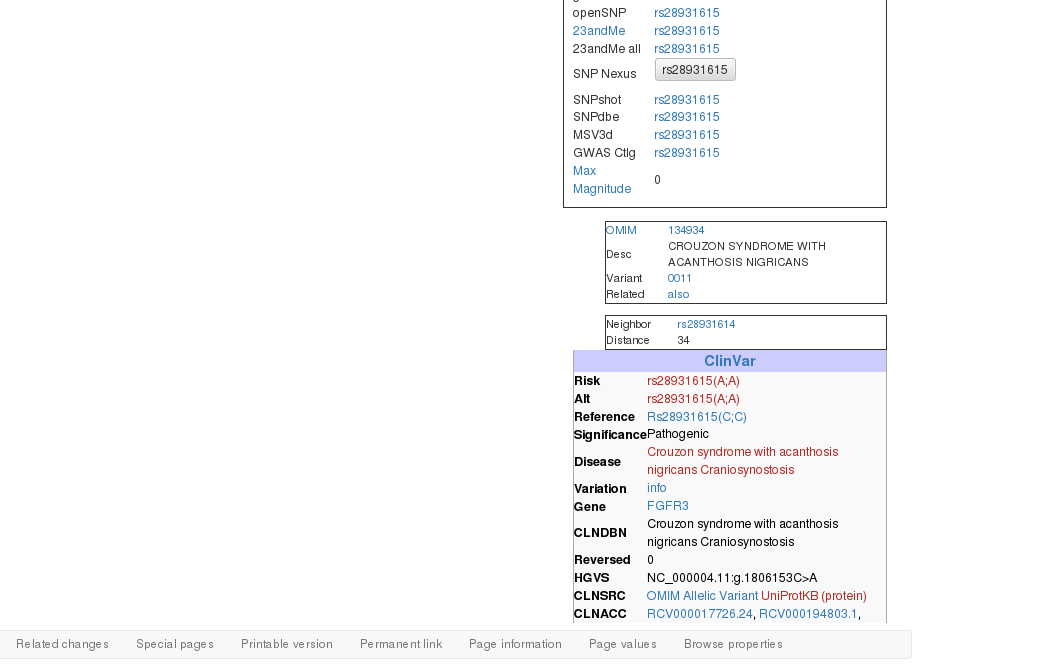
后来发现我们只需要提取里面的部分信息,Orientation,Stabilized,Reference,Chromosome,Position,Gene,还有clinvar表格信息,这时候我们就可以从网页中利用RCurl包,XML包,正则表达是把所需要的内容提取出来,有效抓取有用信息。
知识准备
RCurl包和XML包
在前一篇博文R语言从小木虫网页批量提取考研调剂信息 http://www.cnblogs.com/ywliao/p/6420501.html中已经提过,这里再提一个XML包中之前没有介绍的函数。
readHTMLTable(doc) #doc 是XML或者HTML格式文本,可以是文件名,也可以是刚刚parse的html对象,该函数返回XML或HTML中的表格
正则表达式
这里阐述基本的正则表达式使用 **
[ ]中括号,匹配中括号里面的任意字符,例如[a]匹配"a"
[a-z]表示匹配a到z任意字母,[A-Z]匹配大写A到Z,[0-9]匹配0-9任意数字
[ ]*中括号加*表示匹配任意次,[ ]+表示匹配至少一次,例如[a-zA-z,;: ]+表示匹配小写和大写字母,;:和空格至少一次
[ a|b ] 匹配a或者b
直接输入字符,实现精确定位。比如"apple[a-zA-z,;: ]+",定位到apple开头的后面匹配小写和大写字母,;:和空格至少一次的内容
[\u4E00-\u9FA5]匹配汉字
**
R语言gregexpr函数
使用方法:```gregexpr(pattern,istring, fixed = FALSE) #pattern就是要匹配正则表达是,istring是待匹配的字符串矢量,比如c("abc","cdf"),fixed,
如果设置为true,默认pattern是真正的字符串,不会作为其它使用,相当于转义,
函数返回列表,包括每个字符串的匹配长度和是否匹配)
#实例
 这里直接上代码,代码里面有着详细解释,许多函数以后可以直接复制使用,或者放进一个自己做的R包
!/usr/bin/env Rscript
download <- function(strURL){
输入网址返回html树格式文件
strURL:网页链接地址 return: html树文件
h <- basicTextGatherer()# 查看服务器返回的头信息
txt <- getURL(strURL, headerfunction = h$update,.encoding="gbk") ## 字符串形式
htmlParse(txt,asText=T,encoding="gbk") #选择gbk进行网页的解析
}
getinf <- function(strURL){
主要提取网页信息函数
strURL:网页链接网址 return:包括所要的所有信息的data.frame
doc<- download(strURL)
写如标题
info<- data.frame("Title"=strsplit(xmlValue(getNodeSet(doc,'//title')[[1]])," -")[[1]][1]) #"rs... - SNPedia"进行split
写入"Geno Mag Summary "table
GMS_table <- readHTMLTable(doc)
GMS_index <- 0
if (length(GMS_table)>2){
for (p in 1:6){
if (length(GMS_table[[p]])3){
GMS_index <- p
}
}
}
if (GMS_index!=0){
for (i in 1:length(GMS_table[[GMS_index]])){
tmp <- ""
for (t in 1:nrow(GMS_table[[GMS_index]][i])){
if(tmp""){tmp <-as.vector(GMS_table[[GMS_index]][i][t,1])}else{
tmp <- paste(tmp,as.vector(GMS_table[[GMS_index]][i][t,1]),sep=";")
}
}
if (i1){info$Geno <-tmp}
else if (i2){info$Mag <-tmp}
else if (i==3){info$Summary <- tmp
tmp <- ""
}
}
}else{
info$Geno <-" "
info$Mag <-" "
info$Summary <- " "
}
写入剩下table信息
mes <- getNodeSet(doc,'//td')
mes2 <- list()
for (c in mes){
d <- xmlValue(c)
if (d""){
}else{
mes2=c(mes2,d)
}
}
tmp <- greg_return_string("Make[-A-Za-z0-9_.%;\(\), ]+",mes2)
if (length(tmp)2){info$"Make"=paste(strsplit(tmp[[1]]," ")[[1]][2],strsplit(tmp[[2]]," ")[[1]][2],sep=";")}else{info$"Make"=" "}
for (i in (1:length(pattlistMainTable))){
tmp <- greg_return_index(pattlistMainTable[[i]],mes2)
if (i1 && length(tmp)1){info$"Orientation"=strsplit(mes2[[tmp+1]],"\n")[[1]]}else if (i1 && length(tmp)!=1){info$"Orientation"=" "}
else if (i2 && length(tmp)1){info$"Stabilized"=strsplit(mes2[[tmp+1]],"\n")[[1]]}else if (i2 && length(tmp)!=1){info$"Stabilized"=" "}
else if (i3 && length(tmp)1){info$"Reference"=strsplit(mes2[[tmp+1]],"\n")[[1]]}else if (i3 && length(tmp)!=1){info$"Reference"=" "}
else if (i4 && length(tmp)1){info$"Chromosome"=strsplit(mes2[[tmp+1]],"\n")[[1]]}else if (i4 && length(tmp)!=1){info$"Chromosome"=" "}
else if (i5 &&length(tmp)1){info$"Position"=strsplit(mes2[[tmp+1]],"\n")[[1]]}else if (i5 && length(tmp)!=1){info$"Position"=" "}
else if (i6&&length(tmp)1){info$"Gene"=strsplit(mes2[[tmp+1]],"\n")[[1]]}else if (i6 && length(tmp)!=1){info$"Gene"=" "}
}
写入clivar
mes <- getNodeSet(doc,'//tr')
mes2 <- list()
for (c in mes){
d <- xmlValue(c)
if (d""){
}else{
mes2=c(mes2,d)
}
}
for (i in (1:length(pattlistClinvar))){
tmp <- greg_return_string(pattlistClinvar[i],mes2)
if (length(tmp)!=0){tmp <- tmp[[1]]}
if (i1 && length(tmp)!=0){info$"Risk"=strsplit(tmp,"\n")[[1]][3]}else if (i1 && length(tmp)0){info$"Risk"=" "}
else if (i2 && length(tmp)!=0){info$"Alt"=strsplit(tmp,"\n")[[1]][3]}else if (i2 && length(tmp)0){info$"Alt"=" "}
else if (i3 && length(tmp)!=0){info$"ReferenceBase"=strsplit(tmp,"\n")[[1]][3]}else if (i3&& length(tmp)0){info$"ReferenceBase"=" "}
else if (i4 && length(tmp)!=0){info$"Significance"=strsplit(tmp,"\n")[[1]][2]}else if (i4 && length(tmp)0){info$"Significance"=" "}
else if (i5&& length(tmp)!=0){info$"Disease "=strsplit(tmp,"\n")[[1]][3]}else if (i5 && length(tmp)0){info$"Disease "=" "}
else if (i6 && length(tmp)!=0){info$"CLNDBN"=strsplit(tmp,"\n")[[1]][3]}else if (i6 && length(tmp)0){info$"CLNDBN"=" "}
else if (i7 && length(tmp)!=0){info$"Reversed"=strsplit(tmp,"\n")[[1]][3]}else if (i7 && length(tmp)0){info$"Reversed"=" "}
else if (i8 && length(tmp)!=0){info$"HGVS"=strsplit(tmp,"\n")[[1]][3]}else if (i8 && length(tmp)0){info$"HGVS"=" "}
else if (i9 && length(tmp)!=0){info$"CLNSRC"=strsplit(tmp,"\n")[[1]][3]}else if (i9 && length(tmp)0){info$"CLNSRC"=" "}
else if (i10 && length(tmp)!=0){info$"CLNACC "=strsplit(tmp,"\n")[[1]][3]}else if (i10 && length(tmp)==0){info$"CLNACC "=" "}
}
info
}
greg_return_string <- function(pattern,stringlist){
greg_return_stirng 指定匹配全部字符串列表,返回匹配的字符串
pattern:匹配模式,比如"abc[a-z]*" stringlist:字符串列表,list("abc","abcde","cdfe") return : 列表里字符串匹配结果,"abc""abcde"
findlist <- gregexpr(pattern,stringlist)
needlist <- list()
for (i in which(unlist(findlist)>0)){
preadress <- substr(stringlist[i],findlist[[i]],findlist[[i]]+attr(findlist[[i]],'match.length')-1)
needlist<- c(needlist,list(preadress))
}
return(needlist)
}
greg_return_index <- function(pattern,stringlist){
greg_return_stirng 指定匹配全部字符串列表,返回存在匹配的字符串列表index
pattern:匹配模式 stringlst:待匹配字符串列表 return:存在返回匹配的字符串在列表中的index
findlist <- gregexpr(pattern,stringlist)
needlist <- list()
which(unlist(findlist)>0)
}
extradress <- function(strURL){
将strURL网页里面我们所需要链接提取出来并加工
strURL:网页链接网址 return:网址列表,包括所有提取加工后的网址链接
pattern <- "/index.php/Rs[0-9]+"
prefix <- "https://snpedia.com" #网址改为https起始
links <- getHTMLLinks(download(strURL)) # getHTMLLinks不能解析https的网址,因此先用download解析网址
needlinks <- gregexpr(pattern,links)
needlinkslist <- list()
for (i in which(unlist(needlinks)>0)){
preadress <- substr(links[i],needlinks[[i]],needlinks[[i]]+attr(needlinks[[i]],'match.length')-1)
needlinkslist<- c(needlinkslist,list(preadress))
adresses <- lapply(needlinkslist,function(x)paste(prefix,x,sep=""))
}
adresses
}
greg <- function(pattern,istring){
greg函数查看单个字符串istring,并且返回匹配的部分,不匹配返回空
gregout <- gregexpr(pattern,istring)
substr(istring,gregout[[1]],gregout[[1]]+attr(gregout[[1]],'match.length')-1)
}
library(RCurl)
library(XML)
自定义部分
strURL <- "https://snpedia.com/index.php?title=Special%3ASearch&profile=default&fulltext=Search&search=Congenital+adrenal+hyperplasia" #snpedia网址都已改为https开头
output <- "ouput.txt"
message(paste("[prog]",strURL,output,sep=" "))
strURLs <- extradress(strURL)
pattlistMainTable <- list("Orientation$","Stabilized$","Reference$","Chromosome$","Position$","Gene$")
此匹配模式列表用于返回该字符串所在index,而对应的值是index是该index+1
pattlistClinvar <- list("Risk\n\n[-A-Za-z0-9_.%;\(\), ]+","Alt\n\n[-A-Za-z0-9_.%;\(\), ]+",
"Reference\n\n[-A-Za-z0-9_.%;\(\) ]+","Significance \n[A-Za-z ]+","Disease \n\n[A-Za-z ]+",
"CLNDBN \n\n[-A-Za-z0-9_.% ]+","Reversed \n\n[0-9]+", "HGVS \n\n[-A-Za-z0-9_.%:> ]+","CLNSRC \n\n[-A-Za-z0-9_.% ]+","CLNACC \n\n[-A-Za-z0-9_.%, ]+")
此匹配模式列表用于返回相应clinvar
inf <- NULL
for ( strURL in strURLs){
dat <- getinf(strURL)
if (length(inf) == 0){
inf <- dat
}else{
inf <- rbind(inf,dat)
}
}
write.table(inf, file = output, row.names = F, col.names=T,quote = F, sep="\t") # tab 分隔的文件
message("完成!")
结果可以直接打开,也可以用excel的自文本打开,方便查看
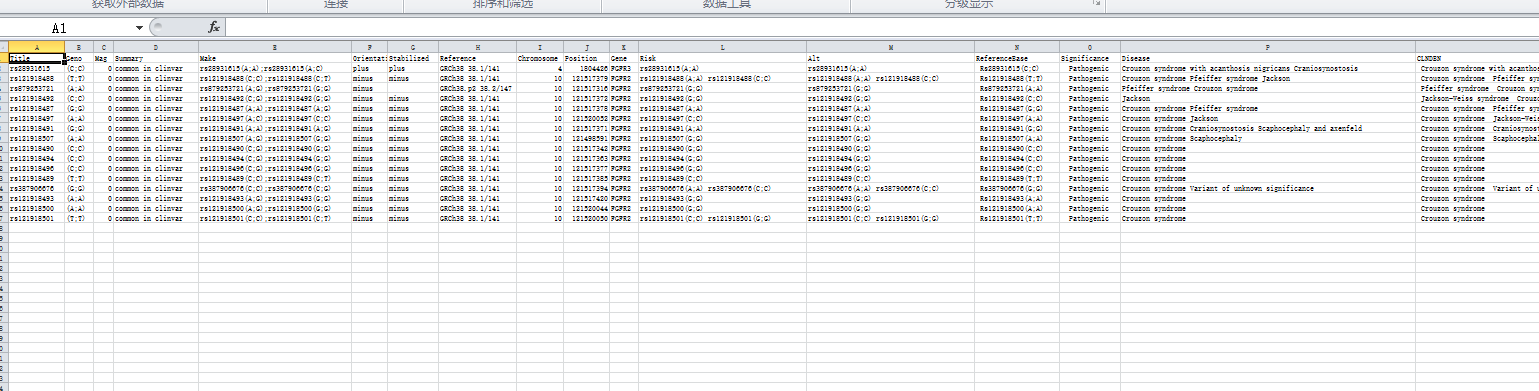寻找与疾病相关的SNP位点——R语言从SNPedia批量提取搜索数据的更多相关文章
- 利用R语言制作出漂亮的交互数据可视化
利用R语言制作出漂亮的交互数据可视化 利用R语言也可以制作出漂亮的交互数据可视化,下面和大家分享一些常用的交互可视化的R包. rCharts包 说起R语言的交互包,第一个想到的应该就是rCharts包 ...
- R语言数据分析利器data.table包—数据框结构处理精讲
R语言数据分析利器data.table包-数据框结构处理精讲 R语言data.table包是自带包data.frame的升级版,用于数据框格式数据的处理,最大的特点快.包括两个方面,一方面是写的快,代 ...
- 使用R语言的RTCGA包获取TCGA数据--转载
转载生信技能树 https://mp.weixin.qq.com/s/JB_329LCWqo5dY6MLawfEA TCGA数据源 - R包RTCGA的简单介绍 - 首先安装及加载包 - 指定任意基因 ...
- R语言基础入门之二:数据导入和描述统计
by 写长城的诗 • October 30, 2011 • Comments Off This post was kindly contributed by 数据科学与R语言 - go there t ...
- 用R语言分析我的fitbit计步数据
目标:把fitbit的每日运动记录导入到R语言中进行分析,画出统计图表来 已有原始数据:fitbit2014年每日的记录电子表格文件,全部数据点此下载,示例如下: 日期 消耗卡路里数 步 距离 攀爬楼 ...
- R语言数据分析利器data.table包 —— 数据框结构处理精讲
R语言data.table包是自带包data.frame的升级版,用于数据框格式数据的处理,最大的特点快.包括两个方面,一方面是写的快,代码简洁,只要一行命令就可以完成诸多任务,另一方面是处理 ...
- R语言data.table包fread读取数据
R语言处理大规模数据速度不算快,通过安装其他包比如data.table可以提升读取处理速度. 案例,分别用read.csv和data.table包的fread函数读取一个1.67万行.230列的表格数 ...
- R语言学习 第三篇:数据框
数据框(data.frame)是最常用的数据结构,用于存储二维表(即关系表)的数据,每一列存储的数据类型必须相同,不同数据列的数据类型可以相同,也可以不同,但是每列的行数(长度)必须相同.数据框的每列 ...
- R语言笔记001——读取csv格式数据
读取csv格式数据 数据来源是西南财经大学 司亚卿 老师的课程作业 方法一:read.csv()函数 file.choose() read.csv("C:\\Users\\Administr ...
随机推荐
- 会话Cookie及session的关系(Cookie & Session)
会话Cookie及session的关系(Cookie & Session) 在通常的使用中,我们只知道session信息是存放在服务器端,而cookie是存放在客户端.但服务器如何使用sess ...
- 模块划分--MVVM指南(课程学习)
实现流水化开发,需要使用“模块划分”的程序开发方式.如此,团队里的每个人负责某项\某几项特定的技术领域,在特定的技术领域更加专业.这样,每个人的效率更高.在专业的技能更熟练,更深入,也会提高队员的成就 ...
- Delphi判断一个字符是否为汉字的最佳方法
//判断字符是否是汉字 function IsHZ(ch: WideChar): boolean; var i:integer; begin i:=ord(ch); if( i<19968) o ...
- #图# #dijkstra# ----- OpenJudge 726:ROADS
OpenJudge 726:ROADS 总时间限制: 1000ms内存限制: 65536kB 描述 N cities named with numbers 1 ... N are connected ...
- C# 程序只能执行一次
应用程序的主入口点. //每一个程序只能运行一个实例 bool isRun = false; System.Threading.Mutex m = new System.Threading.Mutex ...
- ORACLE的Dead Connection Detection浅析
在复杂的应用环境下,我们经常会遇到一些非常复杂并且有意思的问题,例如,我们会遇到网络异常(网络掉包.无线网络断线).客户端程序异常(例如应用程序崩溃Crash).操作系统蓝屏.客户端电脑掉电.死机重启 ...
- [JQuery]serialize()和serializeArray()
1.serialize()把表单的值序列化成字符串 <html> <head> <script src="http://libs.baidu.com/jquer ...
- TSQL编程
1.索引 唯一键/主键添加索引,设计界面,在任何一列前右键--索引/键--点击进入添加某一列为索引 2.视图 视图就是我们查询出来的虚拟表创建视图:create view 视图名 as SQL查询 ...
- SQL SERVER将多行数据合并成一行(转载)
昨天遇到一个SQL Server的问题:需要写一个储存过程来处理几个表中的数据,最后问题出在我想将一个表的一个列的多行内容拼接成一行 比如表中有两列数据 : ep_classes ep_name A ...
- 基于服务的SOA架构_后续篇
今天是元宵节,首先祝各位广大博友在接下来的光阴中技术更上一层,事事如意! 昨天简单介绍了一下本人在近期开发过的一个电商购物平台的架构流程和一些技术说明:今天将详细总结一下在项目中用到的各个架构技术的环 ...
