全网最好看的单细胞umap图绘制教程
全网最好看的单细胞umap图绘制教程
作者按
大家或许都曾被Nature, Science上的单细胞umap图吸引过,不免心生崇拜。在这里,我们将介绍一种简单方便的顶刊级umap图可视化
全文字数|预计阅读时间: 2000|5min
——Starlitnightly(星夜)
环境加载
我们先导入一些必须的依赖包
import omicverse as ov
import scanpy as sc
import matplotlib.pyplot as plt
ov.ov_plot_set()
____ _ _ __
/ __ \____ ___ (_)___| | / /__ _____________
/ / / / __ `__ \/ / ___/ | / / _ \/ ___/ ___/ _ \
/ /_/ / / / / / / / /__ | |/ / __/ / (__ ) __/
\____/_/ /_/ /_/_/\___/ |___/\___/_/ /____/\___/
Version: 1.6.3, Tutorials: https://omicverse.readthedocs.io/
读取数据
我们选取了一个结直肠癌的数据作为演示。
adata=ov.read('crc_50000.h5ad')
adata
AnnData object with n_obs × n_vars = 50000 × 25121
obs: 'n_genes', 'doublet_score', 'predicted_doublet', 'n_genes_by_counts', 'total_counts', 'total_counts_mt', 'pct_counts_mt', 'leiden', 'scsa_celltype', 'major_celltype', 'scsa_true_celltype'
var: 'gene_ids', 'n_cells', 'mt', 'n_cells_by_counts', 'mean_counts', 'pct_dropout_by_counts', 'total_counts', 'highly_variable', 'means', 'dispersions', 'dispersions_norm'
uns: 'dendrogram_leiden', 'hvg', 'leiden', 'leiden_colors', 'leiden_sizes', 'log1p', 'major_celltype_colors', 'neighbors', 'paga', 'pca', 'rank_genes_groups', 'scrublet', 'scsa_celltype_colors', 'umap'
obsm: 'X_pca', 'X_umap'
obsp: 'connectivities', 'distances'
首先我们先尝试一下最基础的umap图绘制可视化
fig, ax = plt.subplots(figsize=(4,4))
ov.pl.embedding(adata,
basis="X_umap",
color=['major_celltype'],
title='',
show=False,
size=10,
frameon='small',
ax=ax
)
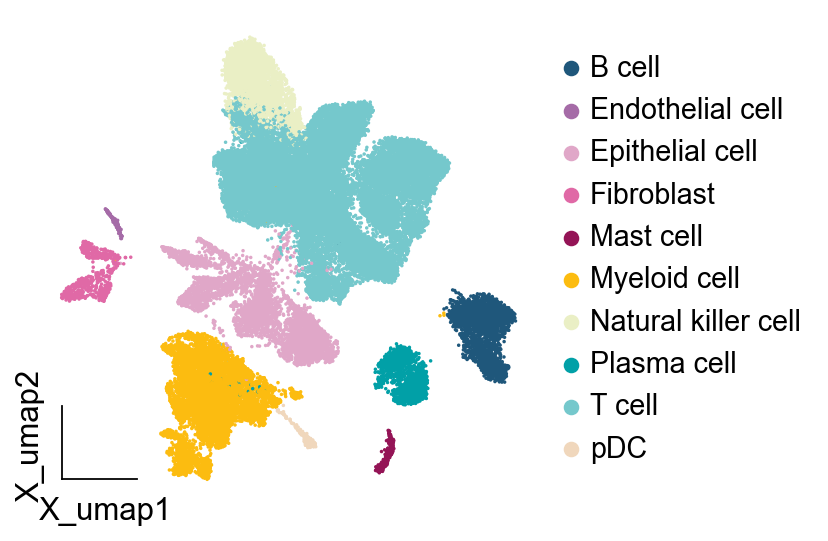
细胞可视化顺序
我们发现效果平平无奇对吧,接下来,我们首先需要修改的是,细胞可视化的顺序,将免疫细胞放到一块,将其他细胞放到另一块
adata.obs['major_celltype'].cat.categories
Index(['B cell', 'Endothelial cell', 'Epithelial cell', 'Fibroblast',
'Mast cell', 'Myeloid cell', 'Natural killer cell', 'Plasma cell',
'T cell', 'pDC'],
dtype='object')
new_order=['B cell', 'Plasma cell','T cell', 'Natural killer cell','Myeloid cell','pDC','Mast cell',
'Endothelial cell', 'Epithelial cell', 'Fibroblast',
]
adata.obs['major_celltype']=adata.obs['major_celltype'].cat.reorder_categories(new_order)
此时我们再可视化,会发现细胞的排序变成了我们指定的顺序
fig, ax = plt.subplots(figsize=(4,4))
ov.pl.embedding(adata,
basis="X_umap",
color=['major_celltype'],title='',
show=False,
frameon='small',
size=10,
ax=ax
)
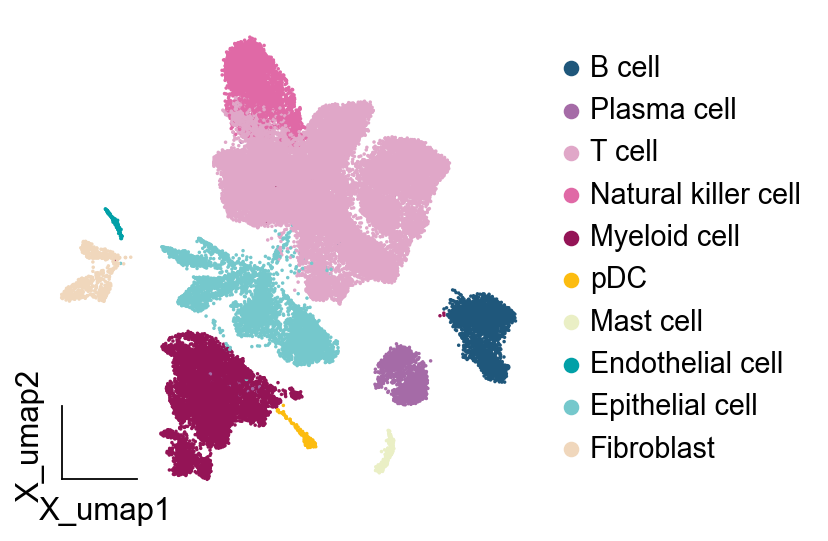
接下来我们再指定细胞类型的颜色,这里有两个方法:
- 第一个方法是我们使用颜色条顺序来指定
- 第二个方法是直接指定细胞类型的颜色
我们先尝试第一个方法,我们希望B细胞是蓝色,T细胞是红色,髓系细胞是绿色,其他细胞是黄色,那么我们根据数量指定颜色条。
需要注意的是,我们在omicverse中提供了5种顶刊级别的颜色条调用
- 红色:
ov.pl.red_color - 蓝色:
ov.pl.blue_color - 橙色:
ov.pl.orange_color - 绿色:
ov.pl.green_color - 紫色:
ov.pl.purple_color
如果你有其他的颜色需求也可以自行指定,颜色条是list格式,例如palette=['#000000','#FFFFFF']
fig, ax = plt.subplots(figsize=(4,4))
ov.pl.embedding(adata,
basis="X_umap",
color=['major_celltype'],title='',
show=False,
size=10,
frameon='small',
palette=ov.pl.blue_color[4:6]+ov.pl.purple_color[1:3]+ov.pl.green_color[:3]+ov.pl.orange_color[:],
ax=ax
)
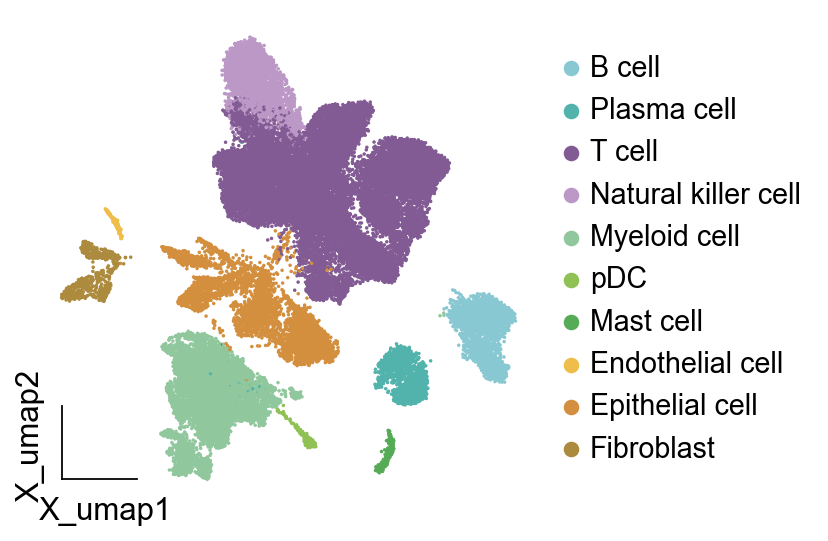
我们发现颜色变成了我们指定的颜色类型
第二种方法也很简单,我们指定每一种细胞类型的颜色然后进行可视化就好了
color_dict={
'B cell':ov.pl.blue_color[4],
'Plasma cell':ov.pl.blue_color[5],
'T cell':ov.pl.purple_color[0],
'Natural killer cell':ov.pl.purple_color[1],
'Myeloid cell':ov.pl.green_color[0],
'pDC':ov.pl.green_color[1],
'Mast cell':ov.pl.green_color[2],
'Endothelial cell':ov.pl.red_color[0],
'Epithelial cell':ov.pl.red_color[1],
'Fibroblast':ov.pl.red_color[2]
}
fig, ax = plt.subplots(figsize=(4,4))
ov.pl.embedding(adata,
basis="X_umap",
color=['major_celltype'],title='',
show=False,
frameon='small',
size=10,
palette=color_dict,
ax=ax
)
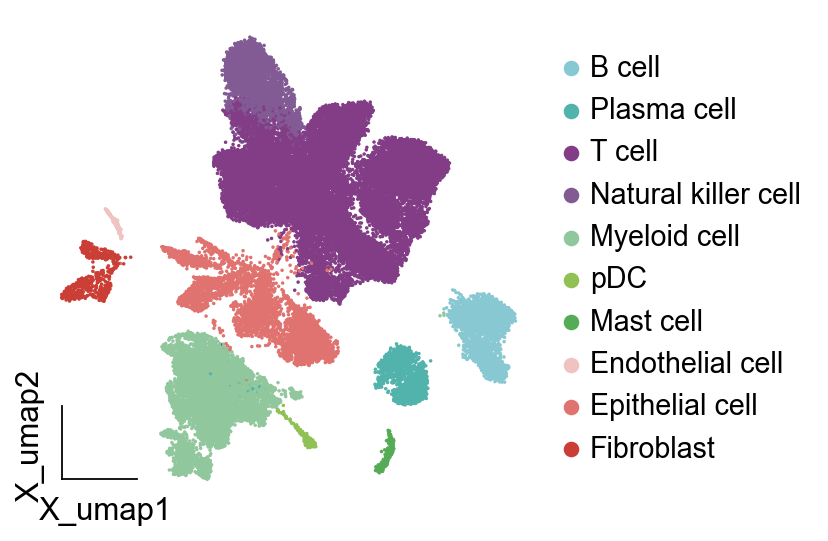
细胞标签优化
我们接下来需要优化的是细胞类型的展示,我们上面绘制的细胞的标签在右边,对于读者而言,需要一个一个去颜色对应的。在Nature最新的出版需求中,希望作者们考虑到色弱等人士的需求,因此我们可以直接在细胞umap图上绘制细胞类型。
需要注意的是,scanpy默认的细胞类型在umap图上的可视化可能出现遮挡,我们在omicverse中提供了新的函数ov.pl.embedding_adjust
from matplotlib import patheffects
fig, ax = plt.subplots(figsize=(4,4))
ov.pl.embedding(adata,
basis="X_umap",
color=['major_celltype'],title='',
show=False, legend_loc=None, add_outline=False,
frameon='small',legend_fontoutline=2,ax=ax
)
ov.pl.embedding_adjust(
adata,
basis="X_umap",
groupby='major_celltype',
ax=ax,
adjust_kwargs=dict(arrowprops=dict(arrowstyle='-', color='black')),
text_kwargs=dict(fontsize=12 ,weight='bold',
path_effects=[patheffects.withStroke(linewidth=2, foreground='w')] ),
)
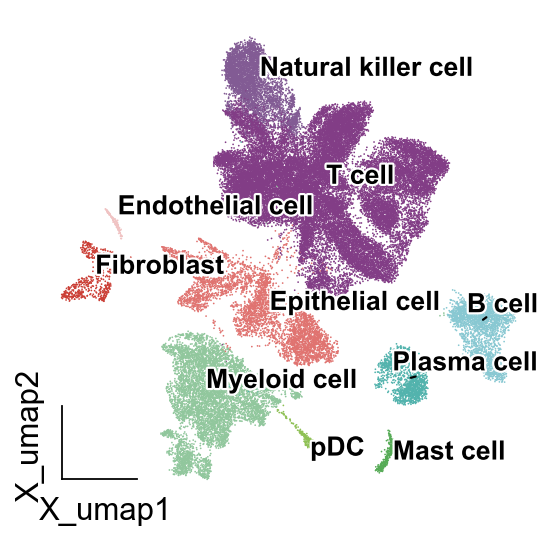
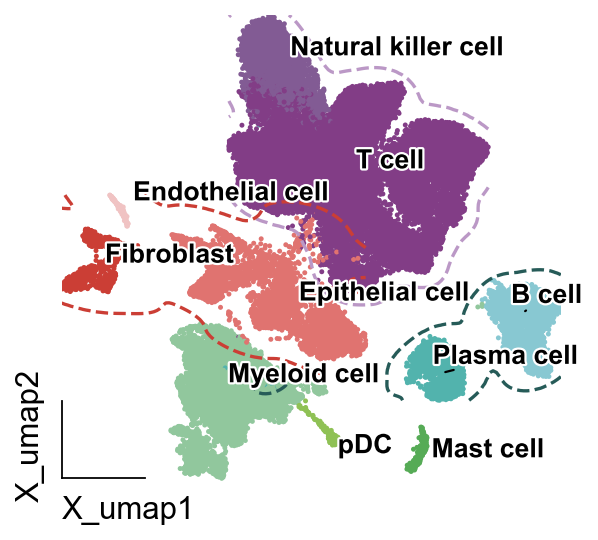
同类细胞轮廓
我们在很多顶刊中会发现,同类细胞往往作者喜欢用轮廓线圈起来,因此,我们在omicverse中也提供了类似的实现。
from matplotlib import patheffects
fig, ax = plt.subplots(figsize=(4,4))
ov.pl.embedding(adata,
basis="X_umap",
color=['major_celltype'],title='',
show=False, legend_loc=None, add_outline=False,
frameon='small',legend_fontoutline=2,ax=ax
)
ov.pl.embedding_adjust(
adata,
basis="X_umap",
groupby='major_celltype',
ax=ax,
adjust_kwargs=dict(arrowprops=dict(arrowstyle='-', color='black')),
text_kwargs=dict(fontsize=12 ,weight='bold',
path_effects=[patheffects.withStroke(linewidth=2, foreground='w')] ),
)
ov.pl.contour(ax=ax,adata=adata,
basis="X_umap",
groupby='major_celltype',clusters=['T cell','Natural killer cell'],
contour_threshold=0.02,colors=ov.pl.red_color[2],linestyles='dashed')
ov.pl.contour(ax=ax,adata=adata,
basis="X_umap",
groupby='major_celltype',clusters=['Plasma cell','B cell'],
contour_threshold=0.01,colors=ov.pl.blue_color[6],linestyles='dashed')
ov.pl.contour(ax=ax,adata=adata,
basis="X_umap",
groupby='major_celltype',clusters=['Endothelial cell', 'Epithelial cell', 'Fibroblast'],
contour_threshold=0.002,colors=ov.pl.orange_color[2],linestyles='dashed')
fig.savefig('umap-ct_major.png',dpi=300,bbox_inches='tight')
fig.savefig('umap-ct_major.pdf',dpi=300,bbox_inches='tight')
以上就是本期教程的全部内容了,如果觉得OmicVerse对你的论文有帮助,不要忘记应用哦,更多单细胞的可视化方法与教程请参考: https://starlitnightly.github.io/omicverse/Tutorials-plotting/t_visualize_single/
全网最好看的单细胞umap图绘制教程的更多相关文章
- Matlab绘图基础——利用axes(坐标系图形对象)绘制重叠图像 及 一图多轴(一幅图绘制多个坐标轴)
描述 axes在当前窗口中创建一个包含默认属性坐标系 axes('PropertyName',propertyvalue,...)创建坐标系时,同时指定它的一些属性,没有指定的使用DefaultAxe ...
- 矢量图绘制工具Svg-edit调整画布的大小
矢量图绘制工具Svg-edit调整画布的大小 ------------------------------ ------------------------
- Matlab 语谱图(时频图)绘制与分析
Matlab 语谱图(时频图)绘制与分析 语谱图:先将语音信号作傅里叶变换,然后以横轴为时间,纵轴为频率,用颜色表示幅值即可绘制出语谱图.在一幅图中表示信号的频率.幅度随时间的变化,故也称" ...
- matplotlib点线 坐标刻度 3D图绘制(六)
plot语句中支持除X,Y以外的参数,以字符串形式存在,来控制颜色.线型.点型等要素,语法形式为: plt.plot(X, Y, 'format', ...) 1 点和线的样式 颜色 参数color或 ...
- 使用JavaScript制作一个好看的轮播图
目录 使用JavaScript制作出好看的轮播图效果 准备材料 1.图片若干张(包括轮播图和按钮的图片) 2.将按钮的图片应用到按钮上的CSS样式文件 3.实现轮播和点击跳转的JavaScript代码 ...
- UML类图绘制
UML图简介 含义:UML-Unified Modeling Language 统一建模语言,又称标准建模语言.是用来对软件密集系统进行可视化建模的一种语言 主要模型: 功能模型:从用户的角度展示系统 ...
- D3力布图绘制--节点自己连自己的实现
案例分析 先看下实现的效果图 实现方法 本篇是在之前写的博文 D3力布图绘制--节点间的多条关系连接线的方法 基础上加修改的,这里放上修改的代码,其他的一样 // DATA var nodes = [ ...
- D3力布图绘制--节点跑掉,单曲线弯曲问题记录
D3力布图绘制中遇到的交互问题,频繁操作数据后,会出现节点跑掉和单曲线弯曲的问题 问题描述 在id指向都正常的情况下出现以下2种状况: 单曲线弯曲 节点跑掉 经排查,是数据重复导致的问题 线条也是一样 ...
- MATLAB之心形图绘制
一.静态心形图绘制 (1)效果展示 (2)静态心形原始代码 clc; clear all; ; % 均布三位坐标 x=-:; y=-:; z=-:; [x,y,z]=meshgrid(x,y,z); ...
- 面向对象的照妖镜——UML类图绘制指南
1.前言 感受 在刚接触软件开发工作的时候,每次接到新需求,在分析需求后的第一件事情,就是火急火燎的打开数据库(DBMS),开始进行数据表的创建工作.然而这种方式,总是会让我在编码过程中出现实体类设计 ...
随机推荐
- 解读注意力机制原理,教你使用Python实现深度学习模型
本文分享自华为云社区<使用Python实现深度学习模型:注意力机制(Attention)>,作者:Echo_Wish. 在深度学习的世界里,注意力机制(Attention Mechanis ...
- 《HelloGitHub》第 98 期
兴趣是最好的老师,HelloGitHub 让你对编程感兴趣! 简介 HelloGitHub 分享 GitHub 上有趣.入门级的开源项目. https://github.com/521xueweiha ...
- 关于Zotero组件在office word中的添加
引言:学姐问我,怎么弄Zotero,在调试过程中遇到的问题及解决方案 Q&A Zotero的安装 找到官网(https://www.zotero.org/)点击download,安装(个人觉得 ...
- 云原生时代的"应用级"多云管理
作者:张齐 当前云计算有多种形态公有云.私有云.边缘云.虚拟机等,如何高效管理多云是当前面临的问题,在云原生时代,又该如何利用云原生技术实现多云管理?本文将讲解通过 Rainbond实现"应 ...
- redis 基础管理
配置文件 优化redis配置文件定制 cat /nosql/redis/6379/redis.conf daemonize yes port 6379 logfile /nosql/redis/637 ...
- 使用kubadm部署一套k8s学习平台环境
使用kubeadm部署k8s集群 环境 IP地址 主机名 节点 10.0.0.63 k8s-master1 master1 10.0.0.63 k8s-master2 master2 10.0.0.6 ...
- vue 的directives一个坑
大江东去,浪淘尽,千古风流人物.故垒西边,人道是,三国周郎赤壁.乱石穿空,惊涛拍岸,卷起千堆雪.江山如画,一时多少豪杰.遥想公瑾当年,小乔初嫁了,雄姿英发.羽扇纶巾,谈笑间,樯橹灰飞烟灭.故国神游,多 ...
- react 装饰器
使用装饰器定义 装饰器是一种函数,写成 @函数名.它可以放在类和类方法的定义前面.react脚手架创建的项目默认是不支持装饰器,需要手动安装相关模块和添加配置文件. 安装相关模块 npm i -D c ...
- lodash已死?radash库方法介绍及源码解析 —— 判断方法篇
前言 大家好,我是阿瓜.一个励志分享更多技术的前端瓜 ~ 我们已经分享了 radash 库中数组.对象等相关的方法,大家感兴趣的可以前往主页查看阅读: 或许你最近在某个地方听过或者看过 radash ...
- 性能分析: 快速定位SQL问题
在数据库性能调优的实践中,SQL性能分析是至关重要的一环.一个执行效率低下的SQL语句可能会导致整个系统的性能瓶颈. 为了快速定位并解决这些问题,我们需要对SQL进行性能分析.本文将介绍一些常用的方法 ...
