KEGG富集分析散点图.md
输入数据格式

pathway = read.table("kegg.result",header=T,sep="\t")
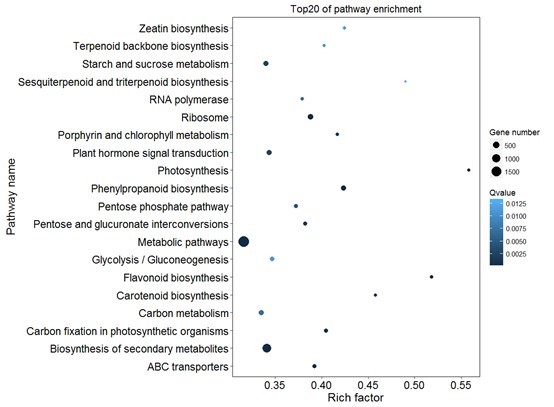
pp = ggplot(pathway,aes(richFactor,Pathway)) #Pathwy是ID,richFactor是富集的基因数目除以背景的基因数目
# 改变点的大小
pp + geom_point(aes(size=R0vsR3)) # 以基因的数目表示点大小
pbubble = pp + geom_point(aes(size=R0vsR3,color=-1*log10(Qvalue))) # 显著性表示颜色
# 自定义渐变颜色
pbubble + scale_colour_gradient(low="green",high="red")
# 绘制pathway富集散点图
pr = pbubble + scale_colour_gradient(low="green",high="red") + labs(color=expression(-log[10](Qvalue)),size="Gene number",x="Rich factor",y="Pathway name",title="Top20 of pathway enrichment")
# 改变图片的样式(主题)去除背景色
pr + theme_bw()
#去除网格线
p_remove_grid <- pr +
theme(panel.grid.major = element_blank(), panel.grid.minor = element_blank())
#网格线颜色
panel.grid=element_line(color='grey')
首先需要安装ggplot2
library(ggplot2) #导入ggplot2
x <- read.table("c:/Users/yueyao/Desktop/pathwayenrichment.txt",head = T, sep = "\t") #读入文件,我的文本文件在桌面
pdf(file="c:/Users/yueyao/Desktop/pathway_enrichment.pdf",width=10,height=10)#生成输出文件,双引号里面为路径及文件名,可自行设置
png(file="c:/Users/yueyao/Desktop/pathway_enrichment.png",width=800,height=800)
p <- ggplot(x,aes(x$Rich.Factor,x$Pathway))#作图利用的两列数据
map = p + geom_point(aes(size=x$Genes,colour=x$Qvalue))+theme(axis.text=element_text(color='black'),axis.text.y=element_text(size=14),axis.text.x=element_text(size=14),panel.background=element_rect(fill='transparent'),panel.grid=element_line(color='grey'),panel.border=element_rect(fill='transparent',color='black'),axis.title=element_text(size=16)) +labs(color="Qvalue",size="Gene number",x="Rich factor",y="Pathway name",title="Top20 of pathway enrichment")
map
dev.off()
输出图片
KEGG富集分析散点图.md的更多相关文章
- 【R】clusterProfiler的GO/KEGG富集分析用法小结
前言 关于clusterProfiler这个R包就不介绍了,网红教授宣传得很成功,功能也比较强大,主要是做GO和KEGG的功能富集及其可视化.简单总结下用法,以后用时可直接找来用. 首先考虑一个问题: ...
- kegg富集分析之:KEGGREST包(9大功能)
这个包依赖极有可能是这个:https://www.kegg.jp/kegg/docs/keggapi.html ,如果可以看懂会很好理解 由于KEGG数据库分享数据的策略改变,因此KEGG.db包不在 ...
- DAVID 进行 GO/KEGG 功能富集分析
何为功能富集分析? 功能富集分析是将基因或者蛋白列表分成多个部分,即将一堆基因进行分类,而这里的分类标准往往是按照基因的功能来限定的.换句话说,就是把一个基因列表中,具有相似功能的基因放到一起,并和生 ...
- python scipy包进行GO富集分析p值计算
最近总是有需要单独对某一个类型的通路进行超几何分布的p值计算,这里记录一下python包的计算方法 使用scipy的stat里面的hypergeom.sf方法进行富集分析的p值计算 hsaxxxxx ...
- GO富集分析 信号通路
基因富集分析是分析基因表达信息的一种方法,富集是指将基因按照先验知识,也就是基因组注释信息进行分类. 信号通路是指能将细胞外的分子信号经细胞膜传入细胞内发挥效应的一系列酶促反应通路.这些细胞外的分子信 ...
- 富集分析DAVID、Metascape、Enrichr、ClueGO
前言 一般我们挑出一堆感兴趣的基因想临时看看它们的功能,需要做个富集分析.虽然公司买了最新版的数据库,如KEGG,但在集群跑下来嫌麻烦.这时网页在线或者本地化工具派上用场了. DAVID DAVID地 ...
- 基因探针富集分析(GSEA)& GO & pathway
http://blog.sina.com.cn/s/blog_4c1f21000100utyx.html GO是Gene Ontology的简称,是生物学家为了衡量基因的功能而而发起的一个项目,从分子 ...
- 利用GSEA对基因表达数据做富集分析
image Gene Set Enrichment Analysis (GSEA) is a computational method that determines whether an a p ...
- R: 修改镜像、bioconductor安装及go基因富集分析
1.安装bioconductor及go分析涉及的相关包 source("http://bioconductor.org/biocLite.R") options(BioC_mirr ...
随机推荐
- 微信小程序微信登录
开发接口 登录 wx.login wx.checkSession 签名加密 小程序登录 小程序可以通过微信官方提供的登录能力方便地获取微信提供的用户身份标识,快速建立小程序内的用户体系. 登录流程时序 ...
- copy()函数技术推演
/*** str_copy.c ***/ #include<stdio.h> void copy_str21(char *from, char *to) { for(; *from != ...
- Python3正则表达式
正则表达式是一个特殊的字符序列,他能帮助你方便的检查一个字符串是否与某种模式匹配. re.match函数 re.match尝试从字符串的起始位置匹配一个模式,如果不是起始位置匹配成功的话,matc ...
- 《挑战30天C++入门极限》C++类的继承与多重继承的访问控制
C++类的继承与多重继承的访问控制 在前面的练习中我们一直在使用public的继承方式,即共有继承方式,对于protected和private继承方式,即保护继承与私有继承方式我们并没有讨论. ...
- Django基础(2)-如何安装特定版本的Django项目
Django1.0版本和2.0版本的差异较大,这里jacky更常用的Django的1.9.8的版本,本小节jacky将给大家分享如何用Pycharm创建1.9.8版本的项目 (一)使用Pycharm配 ...
- 6、httpd2.4 编译安装LAMP
www.itjc8.com 新特性: MPM支持运营DSO机制(动态共享对象),以模块形式按需加载 支持event MPM 支持异步读写 支持每模块及每个目录分别使用各自的日志级别 每请求配置 增强版 ...
- CF1215题解
E 假设从小到大排序,每次交换相邻两个,最小次数即冒泡排序也就是逆序对 考虑值域较小,把每个值映射到\([1,20]\) 设\(f_i\)为已经加入集合为\(i\)的值的最小逆序对个数,考虑填表法 即 ...
- C#题(子文章)(持续更新)
-----> 总文章 入口 文章目录 [-----> 总文章 入口](https://blog.csdn.net/qq_37214567/article/details/90174445) ...
- 2018-2019-2 网络对抗技术 20165212 Exp7 网络欺诈防范
2018-2019-2 网络对抗技术 20165212 Exp7 网络欺诈防范 原理与实践说明 1.实践目标 理解常用网络欺诈背后的原理,以提高防范意识,并提出具体防范方法. 2.实践内容概述 简单应 ...
- arcgis python 拓扑规则
面 Must Not Have Gaps (Area) | Must Not Overlap (Area) 面面 | Must Be Covered By Feature Class Of (Area ...
