6Sampling Configuration Space: 6.3 Using Accelerated Molecular Dynamics (aMD) to enhance sampling
6.3 Using Accelerated Molecular Dynamics (aMD) to enhance sampling
英文官网:http://ambermd.org/tutorials/advanced/tutorial22/index.php
另外可参考 https://blog.chembiosim.com/aMD_in_Amber/
传统的分子动力学允许人们访问数十到数百纳秒的时间尺度; 然而,许多感兴趣的生物过程发生在长达几毫秒或更长时间的较长时间尺度上。
加速动力学是对势能的一种修改——在模拟时减少局域barriers的高度,允许计算得更快。aMD是一个有趣的选择,因为它只需要单个副本的进化,并且它不需要任何关于势能面的先前知识。
aMD 有两种主要版本,一种提高山谷,另一种是降低障碍(山坡)。 后者最近才被引入,它的可用性和好处尚未得到充分研究。 这种方法通常被称为加窗 aMD (w-aMD)。 在本教程中,我们将使用原始的 aMD 公式,但是这两个版本现在都可以在 AMBER 上使用。基础aMD引擎对势能的修改被以下方程定义:
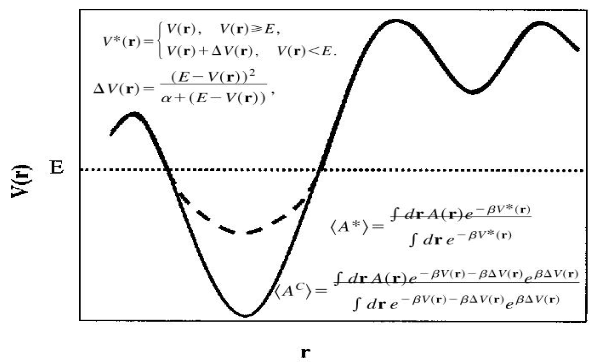
当aMD在AMBER中的实施既可以lowering barriers,又可以raising minima。aMD可以在AMBER的所有MD引擎(sander,pmemd和pmemd.cuda)中实施。The implementation includes the possibility of boosting independently only the torsional terms of the potential (iamd=2) or the whole potential at once (iamd=1). It also allows the possibility to boost the whole potential with an extra boost to the torsions(iamd=3). (目前没搞懂这句的意思)。在aMD中唯一额外需要用户给出的参数是:
a) EthreshP. Average total potential energy threshold. 平均总势能阈值
b) alphaP. Inverse strength boost factor for the total potential energy.总势能的逆强度提升因子
c) EthreshD. Average dihedral energy threshold. 平均二面角能量阈值
d) alphaD. Inverse strength boost factor for the dihedral energy. 二面角能量的逆强度提升因子
本教程将介绍使用aMD的raising minima的采样能力来研究BPTI在微秒时间尺度上发生的构象转变,与毫秒的传统分子动力学模拟进行比较。
Section 1
1) Generating and Relaxing the Initial Structure
普通的MD,将体系平衡。
- Minimize only the water, restraining the protein (20000 cycles)
- Let water move (NTP, 300K), restraining the protein
- Minimize water and protein (20000 cycles)
- Heat the system, restraining the protein (NVT 0 to 300K)
- Relax the system, restraining the protein heavy atoms (NPT, 300K, 0.5ns)
- Relax the system (NPT, 300K, 5ns)
2) Running the aMD calculations and data collection.
有了一个平衡的初始结构后,首先需要运行一个简短的常规MD模拟以收集必要的信息来设置必要的aMD参数。
NSTEP = 39000 TIME(PS) = 6078.000 TEMP(K) = 299.91 PRESS = 94.7
Etot = -39262.0762 EKtot = 7879.4131 EPtot = -47141.4893
BOND = 183.1676 ANGLE = 426.5374 DIHED = 594.3544
1-4 NB = 204.0621 1-4 EEL = 1794.3799 VDWAALS = 7733.9917
EELEC = -58077.9825 EHBOND = 0.0000 RESTRAINT = 0.0000
EKCMT = 3596.2487 VIRIAL = 3332.2057 VOLUME = 129191.4706
Density = 1.0200上述结果只是展示某一帧的能量结果。比如,我们从5ns的MD中获得了 -47,128 kcal/mol 的平均总势能(EPtot)和 595 kcal/mol 的平均二面角(DIHED)能量。 使用这些信息,并考虑到 BPTI 体系有 58 个残基,整个系统 18,226 个原子,我们可以计算 aMD 参数如下:
a) EthreshP: E(tot)= -47128 kcal mol-1 + (0.16kcal*mol-1 atom-1 * 18,226 atoms) = -44212 kcal mol-1
b) alphaP: Alpha(tot)= (0.16kcal mol-1 atom-1 * 18,226 atoms) = 2916 kcal mol-1
c) EthreshD: E(dih)=595 kcal mol-1 + (4kcal mol-1 residue-1 * 58 solute residues) = 827 kcal mol-1
d) alphaD: Alpha(dih)=(1/5)*(4kcal mol-1 residues-1 * 58 solute residues) = 46.4 kcal mol-1
我们现在可以运行完整的 500 ns 模拟,如下所示:
500 ps NVT production
NVT
&cntrl
imin=0,irest=1,ntx=5,
nstlim=250000000,dt=0.002,
ntc=2,ntf=2,ig=-1,
cut=10.0, ntb=1, ntp=0,
ntpr=1000, ntwx=1000,
ntt=3, gamma_ln=2.0,
temp0=300.0,ioutfm=1,iwrap=1,
iamd=3,
ethreshd=827, alphad=46.4,
ethreshp=-44212, alphap=2916,
/
pmemd.cuda -O -i amd.in -o amd.out -p ../*.prmtop -c ../eq.rst -r amd.rst -x prod.nc
3) Analyzing the aMD results
未详细看……
4) Reweighting the aMD results
未详细看……
可以重新加权在模拟中获得的分布,以获得未受干扰的分布。
6Sampling Configuration Space: 6.3 Using Accelerated Molecular Dynamics (aMD) to enhance sampling的更多相关文章
- 机器人学 —— 轨迹规划(Configuration Space)
之前的轨迹规划中,我们只考虑了质点,没有考虑机器人的外形与结构.直接在obstacle map 中进行轨迹规划,然而世纪情况中,机器人有固定外形,可能会和障碍物发生碰撞.此情况下,我们针对机器人自由度 ...
- 机器人运动规划中的构形空间(Configuration Space)
A key concept in motion planning is configuration space, or C-space for short. Every point in the C- ...
- Molecular Dynamics
First]前处理 Second]运行MD Third]后处理 一.获得结构文件-来自实验数据或者某些化学软件工具 1]第一步: 获取并处理pdb文件 从Protein Data Bank下载小肽的p ...
- PCI & PCIE Configuration Register Space
1.PCI-Compatible Configurationbits [1:0] are hard-wired, read-only and must return zeros when read.b ...
- [中英对照]Device Drivers in User Space: A Case for Network Device Driver | 用户态设备驱动: 以网卡驱动为例
前文初步介绍了Linux用户态设备驱动,本文将介绍一个典型的案例.Again, 如对Linux用户态设备驱动程序开发感兴趣,请阅读本文,否则请飘过. Device Drivers in User Sp ...
- Spring源码解析之@Configuration
@Configuration简介 用于标识一个类为配置类,与xml配置效果类似 用法简介 public class TestApplication { public static void main( ...
- Monitoring and Tuning the Linux Networking Stack: Receiving Data
http://blog.packagecloud.io/eng/2016/06/22/monitoring-tuning-linux-networking-stack-receiving-data/ ...
- zhihu spark集群,书籍,论文
spark集群中的节点可以只处理自身独立数据库里的数据,然后汇总吗? 修改 我将spark搭建在两台机器上,其中一台既是master又是slave,另一台是slave,两台机器上均装有独立的mongo ...
- 《Monitoring and Tuning the Linux Networking Stack: Receiving Data》翻译
Overview 从宏观的角度来看,一个packet从网卡到socket接收缓冲区的路径如下所示: 驱动加载并初始化 packet到达网卡 packet通过DMA被拷贝到内核中的一个ring buff ...
- NVIDIA---CUDA
http://en.wikipedia.org/wiki/CUDA CUDA From Wikipedia, the free encyclopedia CUDA Developer(s) N ...
随机推荐
- UntrimmedNets for weakly supervised action recognition and detection概述
0.前言 相关资料: 论文 github 论文解读(CSDN) 论文基本信息: 领域:动作识别与检测 发表时间:CVPR2017(2017.5.22) 1.针对的问题 这篇论文之前的行为识别方法严重依 ...
- mqtt安装和使用
linux下 下载: wget https://www.emqx.io/downloads/broker/v3.2.1/emqx-centos7-v3.2.1.zip 解压:unzip emqx-ce ...
- redhat单网卡配置多个IP
单网卡配置多个IP 进入配置网络的文件目录 复制网络配置文件并修改名字 配置网络 网络1 网络2 激活网络设备 重启网络 重启计算机,查看IP地址 (有问题可以提出来)
- jmeter非GUI模式压测并生成测试报告
关于jmeter非GUI模式压测并生成测试报告 1.脚本调通后,在DOS命令栏进入脚本存在的位置 如果不想通过DOS进入脚本路径,则可以直接指定执行路径,命令如下: JMeter默认去当前目录寻找脚本 ...
- html让容器居中,css让容器水平垂直居中的7种方式
这篇文章主要为大家详细介绍了css让容器水平垂直居中的7种方式,具有一定的参考价值,感兴趣的小伙伴们可以参考一下 这种css布局平时用的比较多,也是面试题常出的一个题,网上一搜一大丢,不过还是想自己总 ...
- Python面向对象编程——__init()__方法
隐式基类object 每个python类都隐式继承object 全文代码实例实现:枚举扑克牌的花色和牌面值 一._init()__方法:对象初始化 显示而非隐式:__init()__应显示展示初始化变 ...
- holiday05
第五天 cat cat会一次性显示所有的内容,适合查看 内容较少 的文本文件 选项 含义 -b 对非空输出行编号 -n 对输出的所有行编号 more more每次只显示一页内容,适合于查看 内容较多 ...
- 攻防世界Web进阶篇——NewsCenter
题目有一个搜索框,下面是搜索结果,最先考虑是sql注入 遇到sql注入,一般先用单引号,1,2尝试.先尝试构造输入为:sd' union select 1,2 #和sd' union select 1 ...
- Java-【Arrays类】和【System类】
Arrays类 [基本介绍] JDK中提供了一个专门用于操作数组的工具类,即Arrays类,位于java util 中. 用前需导包:import java.util.Arrays; [常用方法] 返 ...
- getinstance方法(转)
getinstance方法 https://www.cnblogs.com/roadone/p/7977544.html //实例化 public static DBConnect instance; ...
