RNA-seq 生物学重复相关性验证
根据拿到的表达矩阵设为exprSet
1、用scale 进行标准化
数据中心化:数据集中的各个数字减去数据集的均值
数据标准化:中心化之后的数据在除以数据集的标准差。
在R中利用scale方法来对数据进行中心化和标准化
1 scale(data, center=T, scale=F)
2
3 其中,center为T,表示数据中心化
4
5 scale为T,表示数据标准化
6
7 对一个data frame的每一列进行计算
并不是表达矩阵里面的所有基因都可以进行相关性分析,首先去除reads count >1 小于5个的基因(测试样品共有6个)
1 ##过滤reads count >1 小于5
2 exprSet <- exprSet[apply(exprSet,1, function(x) sum(x>1) >5,]
3 ##reads count 差距较大,用log以及scale 缩小差距
4 M <- scale(cor(llog2(exprSet+1)))
5 ##热图
6 pheatmap(M)
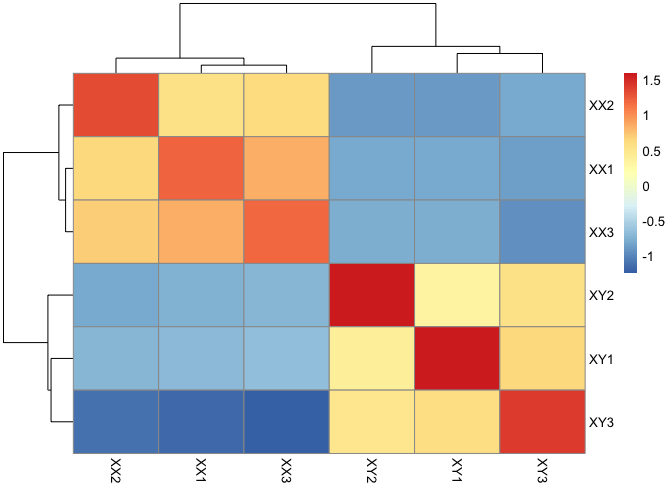
2、另一种标准化
1 exprSet <- exprSet[apply(exprSet,1, function(x) sum(x>1) >5,]
2
3 ##去除文库大小差异
4 exprSet <- log(edgeR::cpm(exprSet)+1)
5
6 ##取mad(绝对中位差)(类似sd)的前50%
7 exprSet <- exprSet[names(sort(apply(exprSet,1,mad),decreasing = T)[1:500]),] ##取前500
8 M <-cor(log2(exprSet+1))
9
10 ##添加group_list
11 tem = data.frame(g=group_list)
12 rownames(tem) <- colnames(M)
13 pheatmap::pheatmap(M, annotation_col = tem,filename = 'cor.png')
3、hclust 聚类分析
欧式距离(Euclidean Distance)
欧式距离是最易于理解的一种距离计算方法,源自欧式空间中两点间的距离公式。
用R语言计算距离主要是dist函数。若X是一个M×N的矩阵,则dist(X)将X矩阵M行的每一行作为一个N维向量,然后计算这M个向量两两间的距离。
表达矩阵是每一行为基因,列为样品名称,所以要进行转至才能计算每个样品之间基因表达量的距离
为了得到更好的聚类分析,也可以将表达矩阵标准化,譬如,log,或者 scale等
1 hc <- hclust(dist(t(exprSet)))
2 plot(hc)
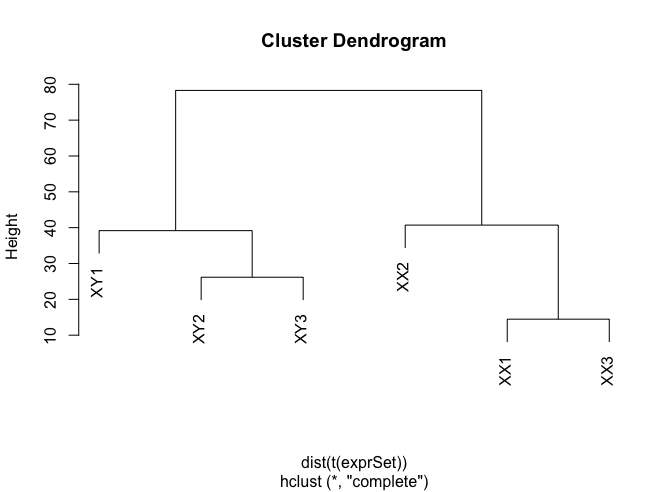
参考:生信技能树
RNA-seq 生物学重复相关性验证的更多相关文章
- 无生物学重复RNA-seq分析 CORNAS: coverage-dependent RNA-Seq analysis of gene expression data without biological replicates
无生物学重复RNA-seq分析 CORNAS: coverage-dependent RNA-Seq analysis of gene expression data without biologic ...
- RNA-seq要做几次生物学重复?找出来的100%都是真正的应答基因
尹师妹:“哈师兄,做验证实验好辛苦,老板让我提高筛选差异基因的条件,尽量降低假阳性,我该怎么筛?” 小哈打开Evernote,给尹师妹看张表: “瞧见那个100%了吗?30 million mappe ...
- RNA seq 两种计算基因表达量方法
两种RNA seq的基因表达量计算方法: 1. RPKM:http://www.plob.org/2011/10/24/294.html 2. RSEM:这个是TCGAdata中使用的.RSEM据说比 ...
- RNA -seq
RNA -seq RNA-seq目的.用处::可以帮助我们了解,各种比较条件下,所有基因的表达情况的差异. 比如:正常组织和肿瘤组织的之间的差异:检测药物治疗前后,基因表达的差异:检测发育过程中,不同 ...
- 使用RDCMan管理SharePoint虚拟机的重复要求验证的问题
首先,这个软件可以从这里下载: Remote Desktop Connection Manager 同类型的软件还有很多,我没有很多复杂功能的要求,就选择了这款微软官方的,虽然很久都没有更新过了. 为 ...
- easy UI的密码长度以及重复输入验证
自己些项目的时候找的时候也找了一会,所以存下来下次用的时候可以直接用了. 话不多说,直接上代码 <tr> <td>密码:</td> <td><in ...
- seq去除重复数据
DELETE FROM temp_fjh_2 a WHERE a.rowid!=(SELECT MAX(b.rowid) FROM temp_fjh_2 b WHERE a.a=b.a); 表名和列名 ...
- 知乎Live总结-重复nature文章笔记Single-cell
来自知乎Live-孟浩巍 1.文章重要技术及图讲解 首先在转录组RNA-seq中,有基因表达差异.基因融合.可变剪切.RNA单点突变. 在基因组中,单点变异.结构变异,CNV变异(拷贝数变异) 三类基 ...
- Circular RNA的产生机制、功能及RNA-seq数据鉴定方法
推荐关注微信公众号:AIPuFuBio,和使用免费生物信息学资源和工具AIPuFu:http://www.aipufu.com. [Circular RNA的产生机制] Circular RNA,缩写 ...
随机推荐
- JVM:内存结构
JVM:内存结构 说明:这是看了 bilibili 上 黑马程序员 的课程 JVM完整教程 后做的笔记 内容 程序计数器 虚拟机栈 本地方法栈 堆 方法区 直接内存 1. 程序计数器 1.1 定义 P ...
- Java:锁笔记
Java:锁笔记 本笔记是根据bilibili上 尚硅谷 的课程 Java大厂面试题第二季 而做的笔记 1. Java 锁之公平锁和非公平锁 公平锁 是指多个线程按照申请锁的顺序来获取锁,类似于排队买 ...
- 2021.9.20考试总结[NOIP模拟57]
(换个编辑器代码就SB地不自动折叠了.. T1 2A 考察快读的写法. $code:$ T1 #include<bits/stdc++.h> #define scanf SCANF=sca ...
- 单片机STM32在开发中常用库函数详解
1.GPIO初始化函数 用法: voidGPIO_Configuration(void) { GPIO_InitTypeDefGPIO_InitStructure;//GPIO状态恢复默认参数 GPI ...
- 计算机网络传输层之TCP流量控制
文章转自:https://blog.csdn.net/weixin_43914604/article/details/105531547 学习课程:<2019王道考研计算机网络> 学习目的 ...
- CODING —— 云原生时代的研发工具领跑者
本文为 CODING 创始人兼 CEO 张海龙在腾讯云 CIF 工程效能峰会上所做的分享. 文末可前往峰会官网,观看回放并下载 PPT. 大家上午好,很高兴能有机会与大家分享 CODING 最近的一些 ...
- hdu 2154 跳舞毯(简单DP)
题意: 有一个圆圆的毯,被平均分成三个扇形.分为标记为A,B,C. 小余从A开始跳,每次可跳到相邻的扇形上.(A->B 或 A->C) 问小余跳n次,最后回到扇形A的方案数是多少. 思路: ...
- springcloud优雅停止上下线与熔断
SpringCloud 服务优雅上下线 Spring Boot 框架使用"约定大于配置"的特性,优雅流畅的开发过程,应用部署启动方式也很优雅.但是我们通常使用的停止应用的方式是 k ...
- Pip安装Django超时(time out)解决方法
(ll_env)learning_log$ pip install Django 执行该命令,始终报错,如上图 解决方法如下: pip install -i http://pypi.douban ...
- Windows漏洞:MS08-067远程代码执行漏洞复现及深度防御
摘要:详细讲解MS08-067远程代码执行漏洞(CVE-2008-4250)及防御过程 本文分享自华为云社区<Windows漏洞利用之MS08-067远程代码执行漏洞复现及深度防御>,作者 ...
